简介
DNA methylation is a process by which methyl groups are added to DNA. Methylation modifies the function of the DNA. When located in a gene promoter, DNA methylation typically acts to repress gene transcription. DNA methylation is essential for normal development and is associated with a number of key processes including genomic imprinting, X-chromosome inactivation, repression of repetitive elements, and carcinogenesis.
DNA methylation at the 5 position of cytosine has the specific effect of reducing gene expression and has been found in every vertebrate examined. In adult somatic cells (cells in the body, not used for reproduction), DNA methylation typically occurs in a CpG dinucleotide context; non-CpG methylation is prevalent in embryonic stem cells,[5][6][7] and has also been indicated in neural development.
原理
在甲基转移酶的催化下,DNA的CG两个核苷酸的胞嘧啶被选择性地添加甲基,形成5-甲基胞嘧啶,这常见于基因的5’-CG-3’序列。大多数脊椎动物基因组DNA都有少量的甲基化胞嘧啶,主要集中在基因5’端的非编码区,并成簇存在。甲基化位点可随DNA的复制而遗传,因为DNA复制后,甲基化酶可将新合成的未甲基化的位点进行甲基化。DNA的甲基化可引起基因的失活,DNA甲基化导致某些区域DNA构象变化,从而影响了蛋白质与DNA的相互作用,甲基化达到一定程度时会发生从常规的B-DNA向Z-DNA的过渡,由于Z-DNA结构收缩,螺旋加深,使许多蛋白质因子赖以结合的原件缩入大沟而不利于转录的起始,导致基因失活。
DNA甲基化主要形成5-甲基胞嘧啶(5-mC)和少量的N6-甲基腺嘌呤(N6-mA)及7-甲基鸟嘌呤(7-mG)。
结构基因编辑
含有很多CpG 结构,2CpG 和2GPC 中两个胞嘧啶的5 位碳原子通常被甲基化,且两个甲基集团在DNA 双链大沟中呈特定三维结构。基因组中60%~ 90% 的CpG 都被甲基化,未甲基化的CpG 成簇地组成CpG 岛,位于结构基因启动子的核心序列和转录起始点。有实验证明超甲基化阻遏转录的进行。DNA 甲基化可引起基因组中相应区域染色质结构变化,使DNA 失去核酶ö限制性内切酶的切割位点,以及DNA 酶的敏感位点,使染色质高度螺旋化,凝缩成团,失去转录活性。5 位C 甲基化的胞嘧啶脱氨基生成胸腺嘧啶,由此可能导致基因置换突变,发生碱基错配: T2G,如果在细胞分裂过程中不被纠正,就会诱发遗传病或癌症,而且,生物体甲基化的方式是稳定的,可遗传的。
The Role of Methylation in Gene Expression
1) Not all genes are active at all times. DNA methylation is one of several epigenetic mechanisms that cells use to control gene expression.
2) 5-azacytidine Experiments Provide Early Clues to the Role of Methylation in Gene Expression.
候选基因CpG岛区域和候选基因甲基化与表观基因组学
1
2
3
4
5
6
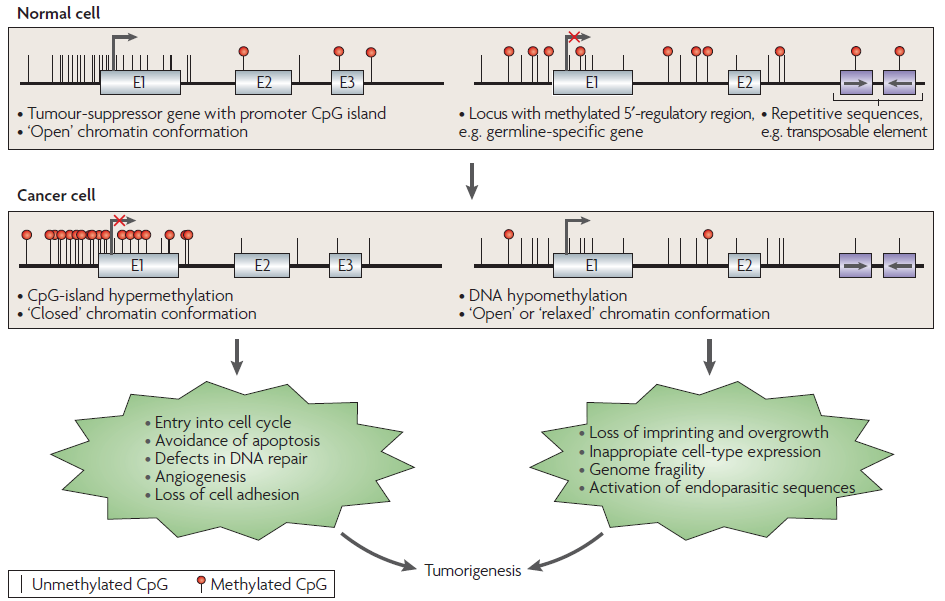
7Figure 1 | Altered DNA-methylation patterns in tumorigenesis. The hypermethylation of CpG islands of tumoursuppressor
genes is a common alteration in cancer cells, and leads to the transcriptional inactivation of these genes
and the loss of their normal cellular functions. This contributes to many of the hallmarks of cancer cells. At the same
time, the genome of the cancer cell undergoes global hypomethylation at repetitive sequences, and tissue-specific
and imprinted genes can also show loss of DNA methylation. In some cases, this hypomethylation is known to
contribute to cancer cell phenotypes, causing changes such as loss of imprinting, and might also contribute to the
genomic instability that characterizes tumours. E, exon.
如图1左所示,在正常细胞中,位于抑癌基因启动子区域的CpG岛处于低水平或未甲基化状态,此时抑癌基因处于正常的开放状态,抑癌基因不断表达抑制肿瘤的发生。而在肿瘤细胞中,该区域的CpG岛被高度甲基化,染色质构象发生改变,抑癌基因的表达被关闭,从而导致细胞进入细胞周期,凋亡丧失,DNA修复缺陷,血管生成以及细胞粘附功能缺失等,最终导致肿瘤发生。同样,如图1右所示,对于在正常细胞中处于高度甲基化的一些基因和重复序列,如果其甲基化水平降低,这些基因将表达和重复序列将激活,从而导致基因印记丢失,细胞过度增长,不合适的细胞特异性表达,基因组脆性增加,以及内寄生序列(endoparasitic sequence)的激活,最终也导致肿瘤发生。
DNA甲基化检测方法
据检测样本不同,可以分为DNA和mRNA。现有方法,绝大部分都是取样于细胞的DNA,根据研究水平,又将这些方法归为3大类,即:基因组甲基化水平(Methylation Content)的分析,候选基因甲基化分析,和基因组层次的DNA甲基化模式(Methylation pattern)与甲基化谱(Methylation Profiling)分析。
基因组甲基化水平(Methylation Content)
高效液相色谱(High-performance Liquid Chromatography, HPLC)
根据DNA或蛋白分子量和构象的不同而使其加以分离。由于在动态相和静态相下分子的光吸收度并不相同而加以定量。随着系统的压强的增加,其分辨率增高。故而能够定量测定基因组整体水平DNA甲基化水平。
过程是将DNA样品先经盐酸或氢氟酸水解成碱基,水解产物通过色谱柱,结果与标准品比较,用紫外光测定吸收峰值及其量,计算5 mC/(5mC+5C)的积分面积就得到基因组整体的甲基化水平。这是一种检测DNA甲基化水平的标准方法。
高效毛细管电泳法(High-performance Capillary Electrophoresis, HPCE)
利用窄孔熔融石英毛细管来从复合物中分离不同化学组分的技术。其基础是在强电场下不同分子的由于其所带电荷,大小,结构以及疏水性等不同而相互分开。用HPCE方法处理DNA水解产物来确定5mC水平,简便,经济且敏感性高。
以上各种方法虽然能够明确检测出目的序列中所有CpG位点的甲基化状况,但并不能对甲基化位点进行定位。
候选基因(Candidate Gene)
甲基化敏感性限制性内切酶-PCR/Southern法( methylation-sensitive restriction Endonuclease -PCR/Southern, MSRE-PCR/Southern)
这种方法利用甲基化敏感性限制性内切酶对甲基化区的不切割的特性,将DNA消化为不同大小的片段后,进行Southern或PCR扩增分离产物,明确甲基化状态再进行分析。常使用的甲基化敏感的限制性内切酶有HpaⅡ-MspⅠ(CCGG)和SmaⅠ-Xmal(CCCGGG)等。
重亚硫酸盐测序法(Bisulphite Sequencing)
该方法首先用重亚硫酸盐使DNA中未发生甲基化的胞嘧啶脱氨基转变成尿嘧啶,而甲基化的胞嘧啶保持不变,行PCR扩增所需片段,则尿嘧啶全部转化成胸腺嘧啶,最后,对PCR产物进行测序并且与未经处理的序列比较,判断是否CpG位点发生甲基化。此方法是精确度很高,能明确目的片段中每一个CpG位点的甲基化状态,但需要大量的克隆测序,过程较为繁琐、昂贵。
甲基化特异性的PCR(methylation-specific PCR, MS-PCR)
该方法同样DNA先用重亚硫酸盐处理,随后行引物特异性的PCR。其设计两对引物,分别与重亚硫酸盐处理后的序列互补配对,即一对结合处理后的甲基化DNA链,另一对结合处理后的非甲基化DNA链。检测MS-PCR扩增产物,如果用针对处理后甲基化DNA链的引物能扩增出片段,则说明该被检测的位点存在甲基化;反之亦然。
甲基化荧光法(MethyLight)
结合重亚硫酸盐处理待测DNA片段,设计一个能与待测位点区互补的探针,探针的5’端连接报告荧光,3’端连接淬灭荧光,随后行实时定量PCR。如果探针能够与DNA杂交,则在PCR用引物延伸时,TaqDNA聚合酶5′到3′端的外切酶活性会将探针序列上5′端的报告荧光切下,淬灭荧光不再能对报告荧光进行抑制,这样报告荧光发光,测定每个循环报告荧光的强度即可得到该位点的甲基化情况及水平。本方法高效,迅速,具备可重复、所需样本量少、不需要电泳分离的特点。
焦磷酸测序(Pyrosequencing)
该方法,由4种酶催化同一反应体系中的酶级联化学发光反应,在每一轮测序反应中,只加入一种dNTP,若该dNTP与模板配对,聚合酶就能将其加入到引物链中并释放出等摩尔数的焦磷酸(PPi)。PPi可最终转化为可见光信号,并由PyrogramTM转化为一个峰值,其高度与核苷酸数目成正比。当用于甲基化检测时,经重亚硫酸盐处理的序列可以看作是C-T型的SNP改变。其操作简单,结果准确可靠,可以行大规模分析。
结合重亚硫酸盐的限制性内切酶法(combined bisulfiterestriction analysis, COBRA)
这种方法对标本DNA行重亚硫酸盐处理及PCR扩增,处理后原甲基化的胞嘧啶被保留,而非甲基化的胞嘧啶变为胸腺嘧啶。随后用限制性内切酶对转化后PCR产物切割的特性以识别原标本DNA的甲基化状况。该方法相对简单,不需预先知道CpG位点及样本序列。
基因组范围的DNA甲基化模式(Methylation pattern)与甲基化谱(Methylation Profiling)
限制性标记基因组扫描(Restriction Landmark Genomic Scanning, RLGS)
RLGS是最早适用于基因组范围DNA甲基化分析的方法之一。该方法先用甲基化敏感的稀频限制性内切酶NotⅠ消化基因组DNA,甲基化位点保留,标记末端、切割、行一维电泳,随后再用更高频的甲基化不敏感的内切酶切割,行二维电泳,这样甲基化的部分被切割开并在电泳时显带,得到RLGS图谱与正常对照得出缺失条带即为甲基化的可能部位。
甲基化间区位点扩增(amplification of inter-methylated sites, AIMS)
AIMS是基于任意引物PCR(Arbitrary Primed PCR)的一种方法,由于任意引物PCR使用寡核苷酸连接子(linker) 进行连接,不需要依赖任何序列的先验信息。在该方法中,用来进行扩增的模板序列首先通过甲基化敏感的限制性内切酶进行消化而富集,其特异性由该酶酶切片断一端的特定序列结合连接子来保证。随后,由内切酶进行第二次消化,再次连接,提纯进行PCR扩增,最后电泳,提取目的序列进行测序。
甲基化CpG岛扩增(Methylated CpG-island amplification, MCA)
MCA也是基于任意引物PCR的方法,该方法使用两种对甲基化具有不同敏感度的限制性内切酶(如SmaI和XmaI)先后进行消化,然后对甲基化敏感的限制性酶切片断进行接头(Adaptor)连接,行PCR,那些富含CpG的序列就会被选择性的扩增。该方法对甲基化分析和克隆甲基化差异性基因都非常有帮助。
差异甲基化杂交(Differential Methylation Hybridization,DMH)
DMH属于一种芯片技术,在该技术中,包括扩增子(Amplicon)生成和CGI文库筛选两个重要组成部分。在扩增子生成中,首先用MseI来酶切DNA样本,然后接上连接子,并去除重复序列,这时的样本一分为二,其一直接进行PCR扩增,生成仅由MseI处理过的扩增子,而另一半则用甲基化敏感的酶BstUI进行消化,然后进行PCR扩增,生成由MseI/BstUI共同处理过的扩增子。CGI文库通过筛查出重复序列,然后进行PCR,选出含有BstUI位点的克隆,最后这些克隆一式两份点到芯片上,制备成CGI芯片。然后把两种不同的扩增子分别杂交到相应的CGI克隆点上,最后通过差异性对比检测出那些未甲基化位点。
由连接子介导PCR出的HpaII小片断富集分析(HpaII tiny fragement Enrichment by Ligation-mediated PCR, HELP)
该方法用HpaII与其对甲基化敏感同裂酶MspI对同一基因组序列进行消化,产生不同的代表性序列,然后对此序列进行连接子介导的PCR,瑞和进行电泳等比较分析或将此DNA样本共杂交到基因组芯片上进行分析。这种方法已经揭示了大量的组织特异性,差异甲基化区域,并用于正常细胞和癌症细胞的基因组比较分析。
甲基化DNA免疫沉淀法(Methylated DNA immunoprecipitation, MeDIP)
这是一种高效富集甲基化DNA的方法。在该方法中,可与5mC特异性结合的抗体加入到变性的基因组DNA片段中,从而使甲基化的基因组片断免疫沉淀,形成富集。通过与已有DNA微芯片技术相结合,从而进行大规模DNA甲基化分析。该方法简便,特异性高,适合DNA甲基化组学(DNA Methylome)的分析。
候选基因甲基化分析网址
http://katahdin.mssm.edu/kismeth/revpage.pl
Contribution from :http://www.nature.com/scitable/topicpage/the-role-of-methylation-in-gene-expression-1070
http://www.nature.com/nrg/journal/v8/n4/full/nrg2005.html
http://www.lifeomics.com/?p=18458
甲基化引物设计
Methyl Primer Express® Software v1.0
https://www.thermofisher.com/order/catalog/product/4376041
